Nat Med | Uma abordagem multiômica para mapear o panorama integrado do tumor, do sistema imunológico e da microbiota do câncer colorretal revela a interação da microbiota com o sistema imunológico
Embora os biomarcadores para câncer colorretal primário tenham sido amplamente estudados nos últimos anos, as diretrizes clínicas atuais baseiam-se apenas no estadiamento TLM (tumor-linfonodo-metástase) e na detecção de defeitos no reparo de erros de pareamento do DNA (MMR) ou instabilidade de microssatélites (MSI) (além dos testes patológicos padrão) para determinar as recomendações de tratamento. Pesquisadores observaram uma falta de associação entre as respostas imunes baseadas na expressão gênica, os perfis microbianos e o estroma tumoral na coorte de câncer colorretal do Atlas do Genoma do Câncer (TCGA) e a sobrevida dos pacientes.
Com o avanço das pesquisas, características quantitativas do câncer colorretal primário, incluindo a natureza celular, imunológica, estromal ou microbiana do câncer, têm demonstrado correlação significativa com os resultados clínicos, mas ainda há um entendimento limitado de como suas interações afetam os desfechos dos pacientes.
Para analisar a relação entre a complexidade fenotípica e o prognóstico, uma equipe de pesquisadores do Instituto Sidra de Pesquisa Médica, no Catar, desenvolveu e validou recentemente um escore integrado (mICRoScore) que identifica um grupo de pacientes com boas taxas de sobrevida, combinando características do microbioma e constantes de rejeição imunológica (ICR). A equipe realizou uma análise genômica abrangente de amostras congeladas de 348 pacientes com câncer colorretal primário, incluindo sequenciamento de RNA de tumores e tecido colorretal saudável correspondente, sequenciamento de exoma completo, sequenciamento profundo do receptor de células T e do gene 16S rRNA bacteriano, complementado por sequenciamento do genoma tumoral completo para caracterizar ainda mais o microbioma. O estudo foi publicado na Nature Medicine com o título “Um atlas integrado de tumor, imunidade e microbioma do câncer de cólon”.

Artigo publicado na Nature Medicine
Visão geral do AC-ICAM
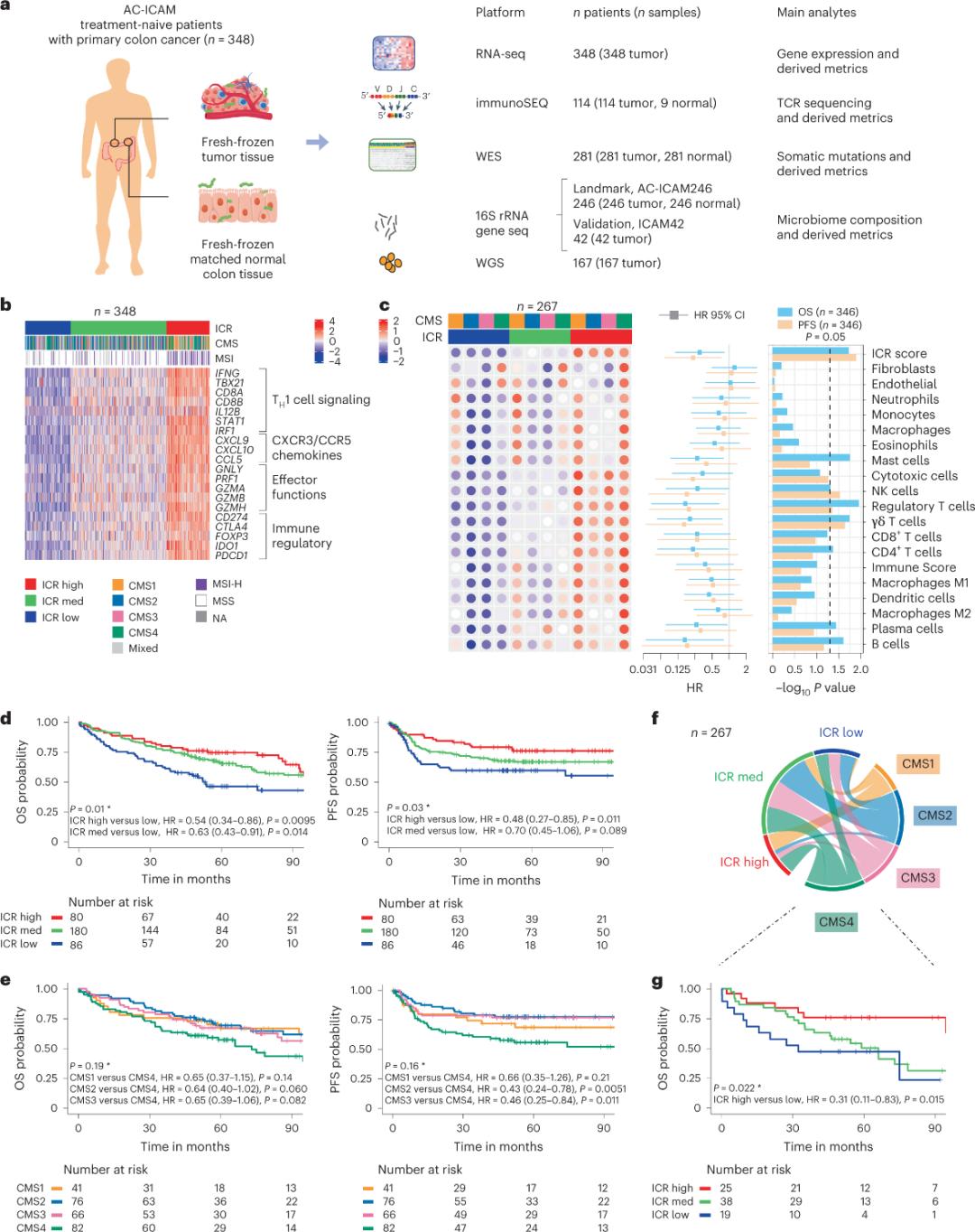
Pesquisadores utilizaram uma plataforma genômica ortogonal para analisar amostras de tumor congeladas e tecido colônico saudável adjacente (pares tumor-normal) de pacientes com diagnóstico histológico de câncer de cólon sem terapia sistêmica. Com base no sequenciamento de exoma completo (WES), controle de qualidade dos dados de RNA-seq e triagem de critérios de inclusão, os dados genômicos de 348 pacientes foram retidos e utilizados para análises subsequentes, com um acompanhamento mediano de 4,6 anos. A equipe de pesquisa denominou esse recurso de Sidra-LUMC AC-ICAM: Um mapa e guia para interações entre imunidade, câncer e microbioma (Figura 1).
Classificação molecular usando ICR
Ao capturar um conjunto modular de marcadores genéticos imunológicos para a imunovigilância contínua do câncer, denominado constante imunológica de rejeição (ICR), a equipe de pesquisa otimizou a ICR condensando-a em um painel de 20 genes que abrange diferentes tipos de câncer, incluindo melanoma, câncer de bexiga e câncer de mama. A ICR também tem sido associada à resposta à imunoterapia em diversos tipos de câncer, incluindo o câncer de mama.
Primeiramente, os pesquisadores validaram a assinatura ICR da coorte AC-ICAM, utilizando uma abordagem de co-classificação baseada no gene ICR para classificar a coorte em três grupos/subtipos imunológicos: ICR alto (tumores quentes), ICR médio e ICR baixo (tumores frios) (Figura 1b). Os pesquisadores caracterizaram a propensão imunológica associada aos subtipos moleculares de consenso (CMS), uma classificação do câncer de cólon baseada no transcriptoma. As categorias CMS incluíram CMS1/imune, CMS2/canônico, CMS3/metabólico e CMS4/mesenquimal. A análise mostrou que os escores de ICR apresentaram correlação negativa com certas vias de células cancerígenas em todos os subtipos CMS, e correlações positivas com vias imunossupressoras e relacionadas ao estroma foram observadas apenas em tumores CMS4.
Em todos os CMS, a abundância de células natural killer (NK) e subconjuntos de células T foi maior nos subtipos imunes com ICR alto, com maior variabilidade em outros subconjuntos de leucócitos (Figura 1c). Os subtipos imunes de ICR apresentaram sobrevida global (SG) e sobrevida livre de progressão (SLP) diferentes, com um aumento progressivo de ICR de baixo para alto (Figura 1d), validando o papel prognóstico do ICR no câncer colorretal.
Figura 1. Desenho do estudo AC-ICAM, assinatura genética relacionada à imunidade, subtipos imunológicos e moleculares e sobrevida.
O ICR captura células T amplificadas clonalmente e enriquecidas em tumores.
Apenas uma minoria das células T que infiltram o tecido tumoral apresenta especificidade para antígenos tumorais (menos de 10%). Portanto, a maioria das células T intratumorais é denominada células T espectadoras (células T de observação). A correlação mais forte com o número de células T convencionais com TCRs produtivos foi observada em subpopulações de células estromais e leucócitos (detectadas por RNA-seq), que podem ser usadas para estimar subpopulações de células T (Figura 2a). Nos agrupamentos de ICR (classificação geral e CMS), a maior clonalidade de TCRs de sequência imune foi observada nos grupos ICR-alto e subtipo CMS1/imune (Figura 2c), com a maior proporção de tumores ICR-alto. Usando o transcriptoma completo (18.270 genes), seis genes de ICR (IFNG, STAT1, IRF1, CCL5, GZMA e CXCL10) estavam entre os dez principais genes positivamente associados à clonalidade de TCR de sequência imune (Figura 2d). A clonalidade do TCR determinada por ImmunoSEQ apresentou correlação mais forte com a maioria dos genes ICR do que as correlações observadas com marcadores CD8+ responsivos a tumores (Figuras 2f e 2g). Em conclusão, a análise acima sugere que a assinatura ICR captura a presença de células T amplificadas clonalmente e enriquecidas em tumores, podendo explicar suas implicações prognósticas.
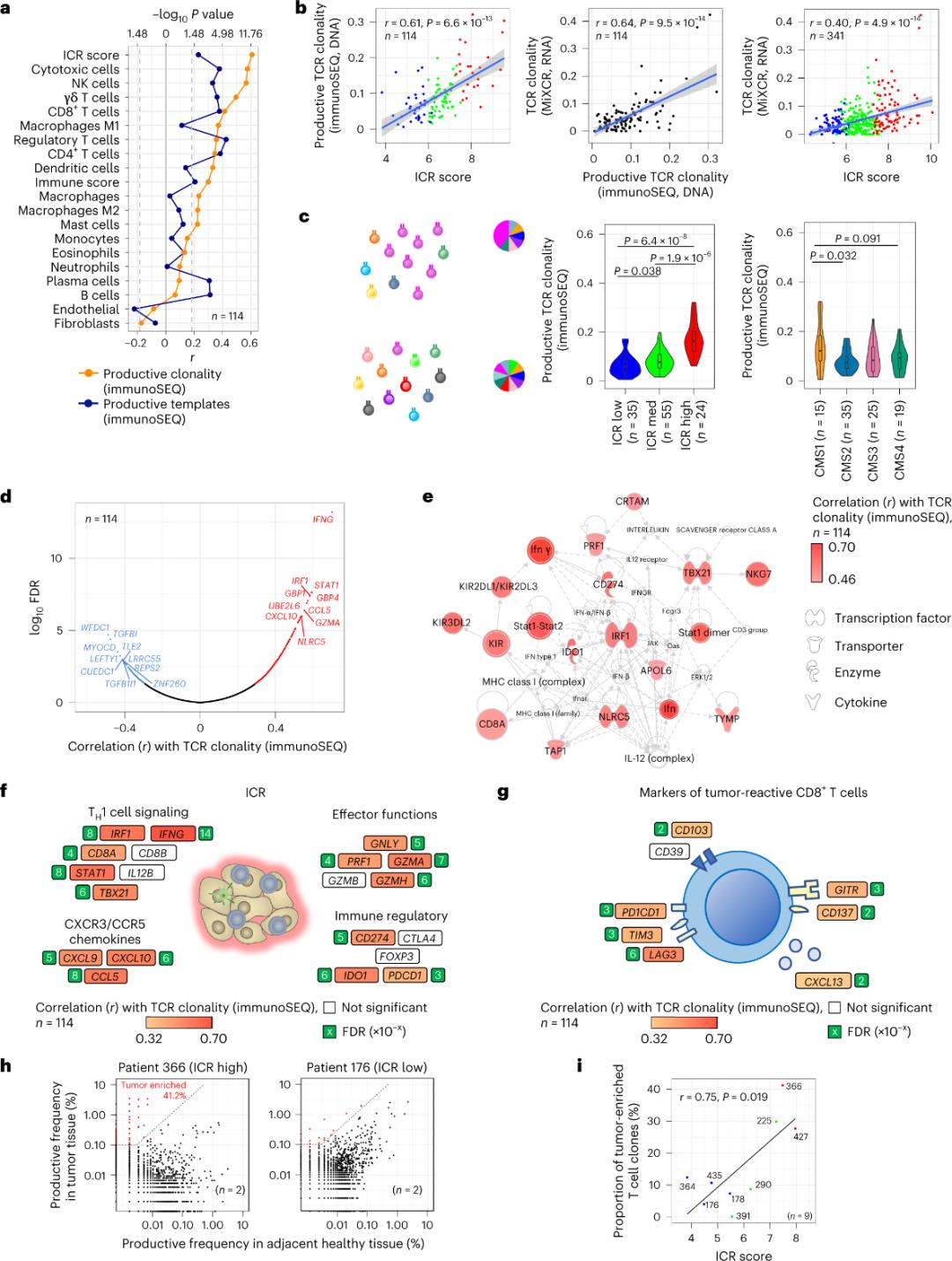
Figura 2. Métricas do TCR e correlação com genes relacionados à imunidade, subtipos imunes e moleculares.
Composição do microbioma em tecidos saudáveis e com câncer de cólon
Os pesquisadores realizaram o sequenciamento do rRNA 16S utilizando DNA extraído de tecido tumoral e tecido colônico saudável pareados de 246 pacientes (Figura 3a). Para validação, os pesquisadores também analisaram dados de sequenciamento do gene rRNA 16S de outras 42 amostras tumorais que não possuíam DNA normal pareado disponível para análise. Primeiramente, os pesquisadores compararam a abundância relativa da microbiota entre os tumores e o tecido colônico saudável pareados. Observou-se um aumento significativo de Clostridium perfringens nos tumores em comparação com as amostras saudáveis (Figuras 3a-3d). Não houve diferença significativa na diversidade alfa (diversidade e abundância de espécies em uma única amostra) entre as amostras tumorais e saudáveis, e uma redução modesta na diversidade microbiana foi observada em tumores com alta expressão de ICR em relação aos tumores com baixa expressão de ICR.
Para detectar associações clinicamente relevantes entre perfis microbianos e desfechos clínicos, os pesquisadores buscaram utilizar dados de sequenciamento do gene 16S rRNA para identificar características do microbioma que predizem a sobrevida. No estudo AC-ICAM246, os pesquisadores executaram um modelo de regressão de Cox para sobrevida global que selecionou 41 características com coeficientes diferentes de zero (associadas a risco diferencial de mortalidade), denominadas classificadores MBR (Figura 3f).
Nesta coorte de treinamento (ICAM246), uma baixa pontuação de MBR (MBR<0, MBR baixa) foi associada a um risco significativamente menor de morte (85%). Os pesquisadores confirmaram a associação entre baixa MBR (risco) e sobrevida global prolongada em duas coortes validadas independentemente (ICAM42 e TCGA-COAD). (Figura 3) O estudo mostrou uma forte correlação entre cocos endogástricos e pontuações de MBR, que foram semelhantes no tecido tumoral e no tecido colônico saudável.
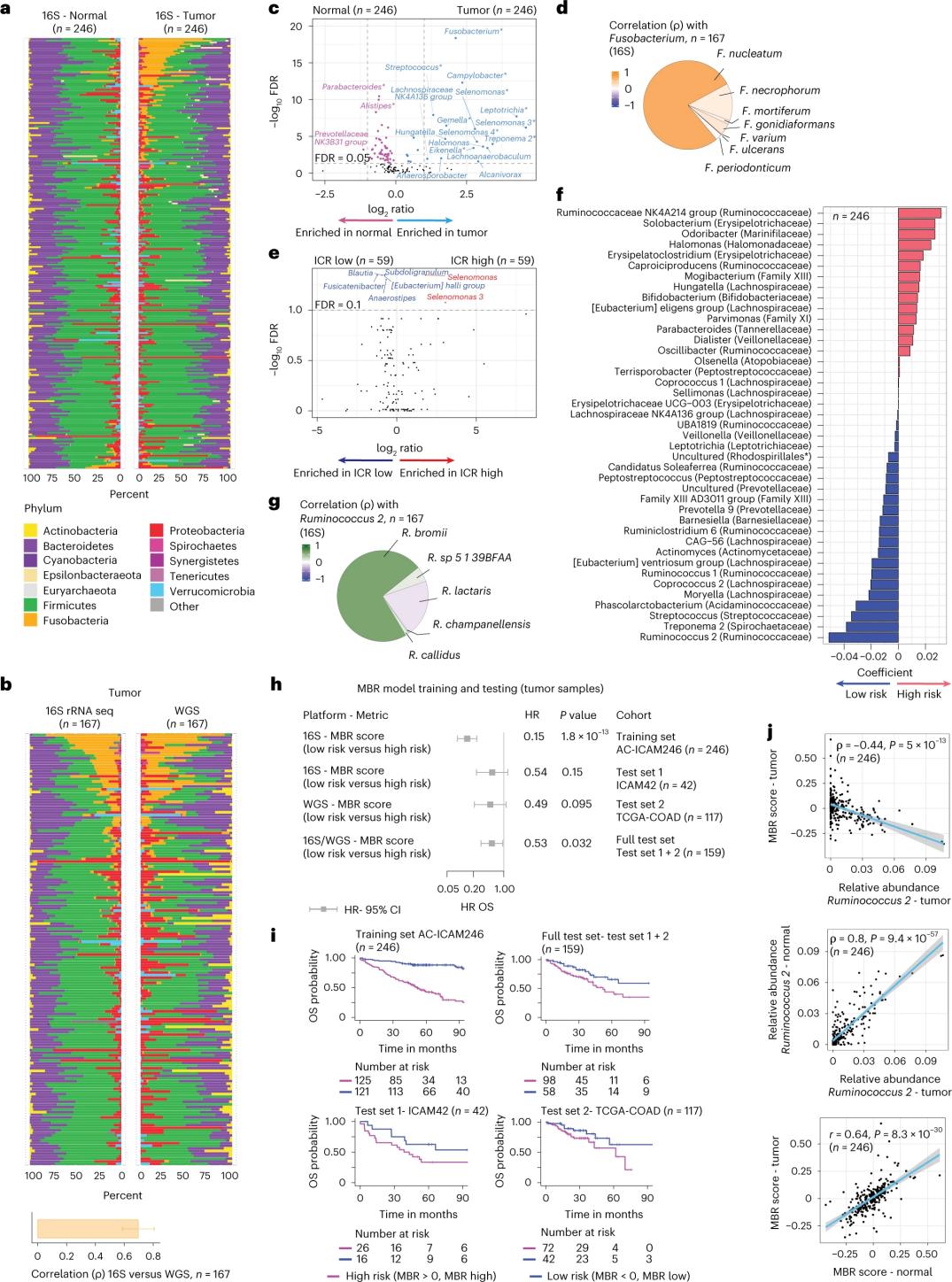
Figura 3. Microbioma em tecidos tumorais e saudáveis e sua relação com a taxa de resposta imune (ICR) e a sobrevida do paciente.
Conclusão
A abordagem multiômica utilizada neste estudo permite a detecção e análise minuciosas da assinatura molecular da resposta imune no câncer colorretal e revela a interação entre o microbioma e o sistema imunológico. O sequenciamento profundo do TCR em tecidos tumorais e saudáveis revelou que o efeito prognóstico do ICR pode ser atribuído à sua capacidade de capturar clones de células T enriquecidos em tumores e possivelmente específicos para antígenos tumorais.
Ao analisar a composição do microbioma tumoral por meio do sequenciamento do gene 16S rRNA em amostras de AC-ICAM, a equipe identificou uma assinatura do microbioma (escore de risco MBR) com forte valor prognóstico. Embora essa assinatura tenha sido derivada de amostras tumorais, houve uma forte correlação entre o cólon e o reto saudáveis e o escore de risco MBR do tumor, sugerindo que essa assinatura pode capturar a composição do microbioma intestinal dos pacientes. Combinando os escores ICR e MBR, foi possível identificar e validar um biomarcador multiômico que prediz a sobrevida em pacientes com câncer de cólon. O conjunto de dados multiômicos do estudo fornece um recurso para melhor compreender a biologia do câncer de cólon e auxiliar na descoberta de abordagens terapêuticas personalizadas.
Data da publicação: 15 de junho de 2023
 中文网站
中文网站